PPI網路實戰:String加CytoScape聯手挖掘PPI網路
歡迎關注微信公眾號《生信修煉手冊》!
在之前的文章中,我們提到利用網路聚類演算法可以從複雜的蛋白質網路中挖掘蛋白複合體或者相應的功能模組,其中MCODE演算法是最常用的挖掘蛋白複合體的演算法。
MCODE全稱molecular complex detection, 是最廣泛使用的挖掘蛋白複合體的演算法之一,在cytoscape 軟體中提供了一個MCODE外掛,可以方便的對網路進行聚類。
cytoscape 是一個功能強大的網路視覺化軟體,除了基本的視覺化之外,通過各種外掛,還可以輕鬆的實現各種資料分析,外掛的下載地址如下
眾多外掛中,也可以看到MCODE外掛的下載使用率名列前茅。

在下載外掛時,建議先開啟cytoscape軟體,這樣可以直接線上安裝,非常方便。
構建PPI網路,我們需要一個基因列表,比如轉錄組分析得到的差異基因列表,然後到String網站上,進行檢索,示意如下

檢索之後,下載tsv格式的結果檔案,示意如下

在該檔案中,前兩列的資訊是我們需要的,內容如下
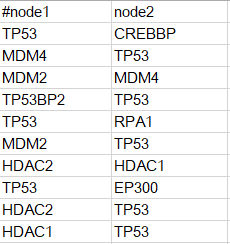
擷取前兩列,然後另存為一個檔案,通常叫做edge.txt。這個檔案可以直接匯入cytsocape軟體,通過File->Import->Network->File, 將該檔案匯入,匯入之後,通過Apps->MCODE, 啟動MCODE外掛,在控制面板,可以看到下圖

選擇預設引數,對整個網路繼續聚類,在右側的結果面板可以看到如下所示的結果

聚類之後會得到多個子網subnetwork, 對於每個子網,可以看到其節點數,邊數,打分值等基本資訊,所有子網的資訊可以通過Export按鈕匯出到檔案中,如下所示
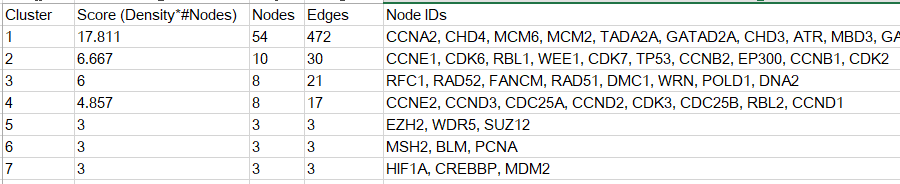
點選每個子網,通過在中間面板看到該子網的視覺化結果,示意如下

然後可以自定義的調整各項引數,使圖片更加美觀。通過MCODE外掛,我們可以方便的得到複雜的PPI網路中潛在的各個子網,但是後續還是要結合功能註釋,比如KEGG,蛋白複合物資料庫的註釋等,對結果進一步解讀。
掃描關注微訊號,更多精彩內容等著你!

