資料科學和人工智慧技術筆記 七、特徵工程
阿新 • • 發佈:2018-12-28
七、特徵工程
作者:Chris Albon
譯者:飛龍
稀疏特徵矩陣上的降維
# 載入庫
from sklearn.preprocessing import StandardScaler
from sklearn.decomposition import TruncatedSVD
from scipy.sparse import csr_matrix
from sklearn import datasets
import numpy as np
# 載入資料
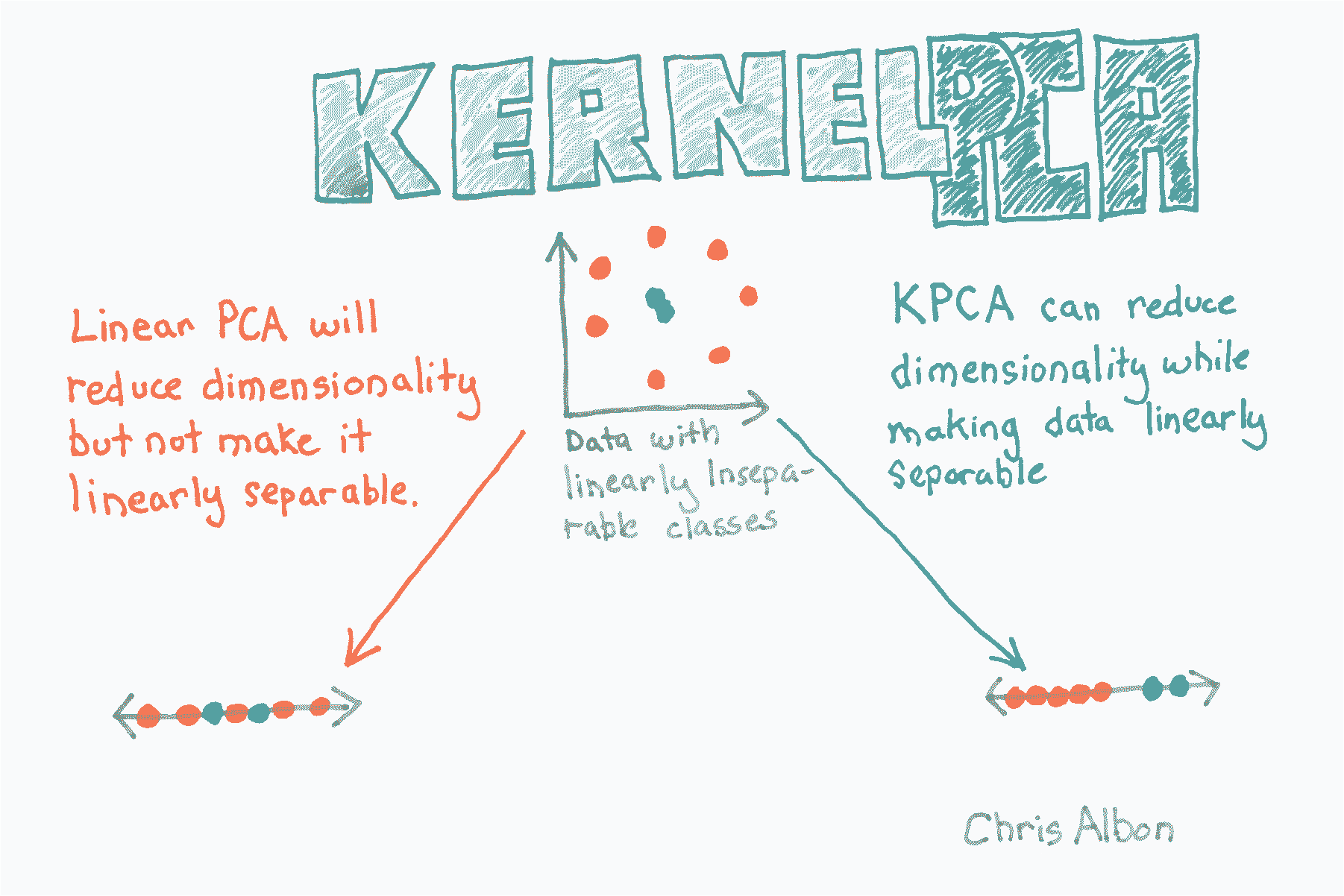
digits = datasets.load_digits( 核 PCA 降維
# 載入庫
from sklearn.decomposition import PCA, KernelPCA
from sklearn.datasets import make_circles
# 建立線性不可分的資料 使用 PCA 的降維
# 載入庫
from sklearn.preprocessing import StandardScaler
from sklearn.decomposition import PCA
from sklearn import datasets
# 載入資料
digits = datasets.load_digits()
# 標準化特徵矩陣
X = StandardScaler().fit_transform(digits.data)
# 建立保留 99% 方差的 PCA
pca = PCA(n_components=0.99, whiten=True)
# 使用 PCA
X_pca = pca.fit_transform(X)
# 展示結果
print('Original number of features:', X.shape[1])
print('Reduced number of features:', X_pca.shape[1])
'''
Original number of features: 64
Reduced number of features: 54
'''
PCA 特徵提取
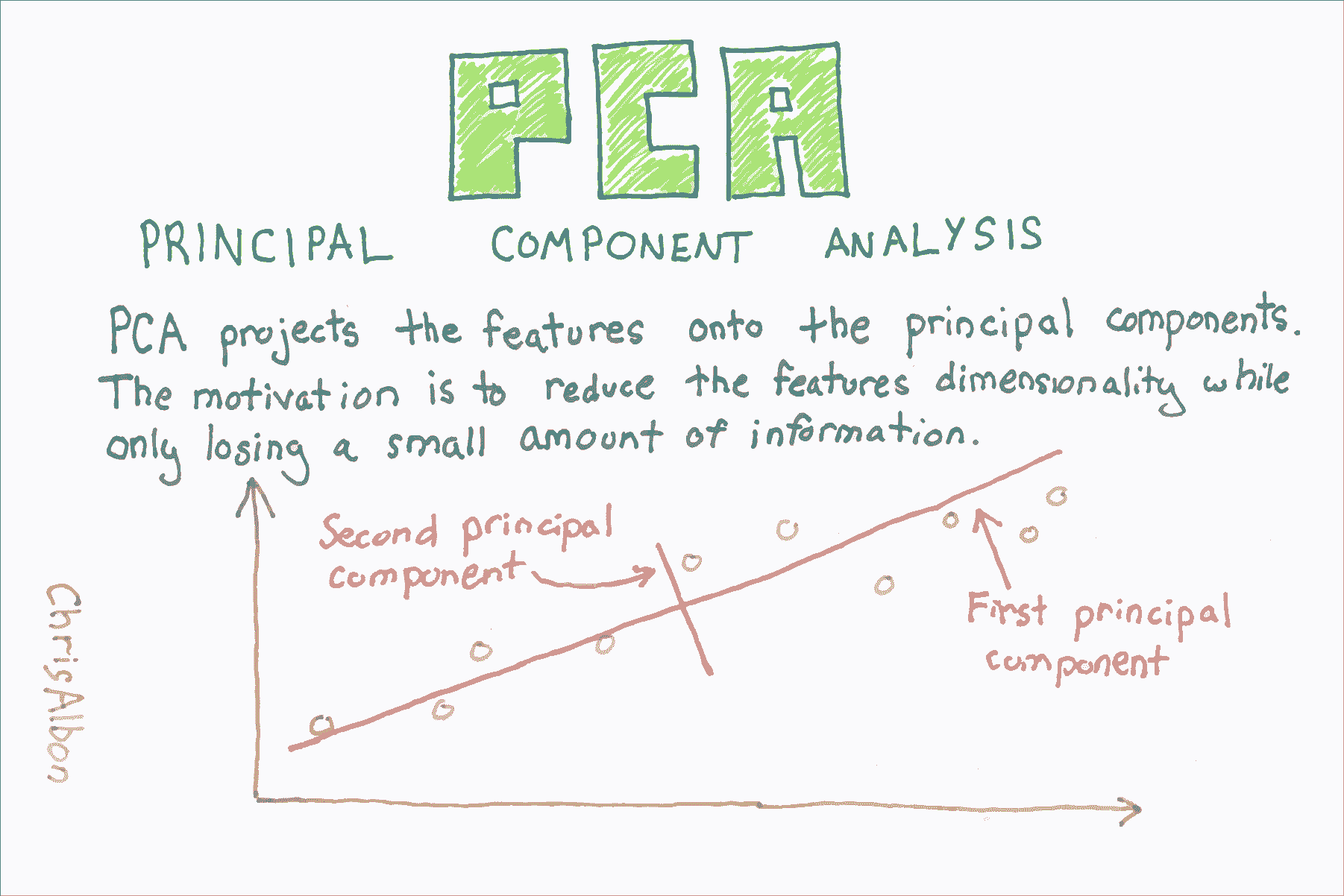
主成分分析(PCA)是資料科學中常見的特徵提取方法。 從技術上講,PCA 找到具有最高特徵值的協方差矩陣的特徵向量,然後使用這些特徵向量將資料投影到相等或更小維度的新子空間。 實際上,PCA 將 n 個特徵矩陣轉換為(可能)小於 n 個特徵的新資料集。 也就是說,它通過構造新的較少變數來減少特徵的數量,這些變數捕獲原始特徵中找到的資訊的重要部分。 但是,本教程的目的不是要解釋 PCA 的概念,這在其他地方做得非常好,而是用於演示 PCA 的實際應用。
# 匯入庫
import numpy as np
from sklearn import decomposition, datasets
from sklearn.preprocessing import StandardScaler
# 載入乳腺癌資料集
dataset = datasets.load_breast_cancer()
# 載入特徵
X = dataset.data
請注意,原始資料包含 569 個觀測和 30 個特徵。
# 檢視資料集的形狀
X.shape
# (569, 30)
這裡是資料的樣子
# 檢視資料
X
'''
array([[ 1.79900000e+01, 1.03800000e+01, 1.22800000e+02, ...,
2.65400000e-01, 4.60100000e-01, 1.18900000e-01],
[ 2.05700000e+01, 1.77700000e+01, 1.32900000e+02, ...,
1.86000000e-01, 2.75000000e-01, 8.90200000e-02],
[ 1.96900000e+01, 2.12500000e+01, 1.30000000e+02, ...,
2.43000000e-01, 3.61300000e-01, 8.75800000e-02],
...,
[ 1.66000000e+01, 2.80800000e+01, 1.08300000e+02, ...,
1.41800000e-01, 2.21800000e-01, 7.82000000e-02],
[ 2.06000000e+01, 2.93300000e+01, 1.40100000e+02, ...,
2.65000000e-01, 4.08700000e-01, 1.24000000e-01],
[ 7.76000000e+00, 2.45400000e+01, 4.79200000e+01, ...,
0.00000000e+00, 2.87100000e-01, 7.03900000e-02]])
'''
# 建立縮放器物件
sc = StandardScaler()
# 使縮放器擬合特徵並轉換
X_std = sc.fit_transform(X)
請注意,PCA 包含一個引數,即成分數。 這是輸出特徵的數量,需要進行調整。
# 建立 PCA 物件,使用兩個成分作為引數
pca = decomposition.PCA(n_components=2)
# 擬合 PCA 並轉換資料
X_std_pca = pca.fit_transform(X_std)
在 PCA 之後,新資料已降到了兩個特徵,其行數與原始特徵相同。
# 檢視新特徵資料的形狀
X_std_pca.shape
# (569, 2)
# 檢視新特徵資料
X_std_pca
'''
array([[ 9.19283683, 1.94858307],
[ 2.3878018 , -3.76817174],
[ 5.73389628, -1.0751738 ],
...,
[ 1.25617928, -1.90229671],
[ 10.37479406, 1.67201011],
[ -5.4752433 , -0.67063679]])
'''
使用 KMeans 聚類對觀測分組
# 載入庫
from sklearn.datasets import make_blobs
from sklearn.cluster import KMeans
import pandas as pd
# 製作模擬特徵矩陣
X, _ = make_blobs(n_samples = 50,
n_features = 2,
centers = 3,
random_state = 1)
# 建立 DataFrame
df = pd.DataFrame(X, columns=['feature_1','feature_2'])
# 建立 KMeans 聚類器
clusterer = KMeans(3, random_state=1)
# 擬合聚類器
clusterer.fit(X)
'''
KMeans(algorithm='auto', copy_x=True, init='k-means++', max_iter=300,
n_clusters=3, n_init=10, n_jobs=1, precompute_distances='auto',
random_state=1, tol=0.0001, verbose=0)
'''
# 預測值
df['group'] = clusterer.predict(X)
# 前幾個觀測
df.head(5)
| feature_1 | feature_2 | group | |
|---|---|---|---|
| 0 | -9.877554 | -3.336145 | 0 |
| 1 | -7.287210 | -8.353986 | 2 |
| 2 | -6.943061 | -7.023744 | 2 |
| 3 | -7.440167 | -8.791959 | 2 |
| 4 | -6.641388 | -8.075888 | 2 |
為 LDA 選擇最佳數量的成分
在 scikit-learn 中,LDA 是使用LinearDiscriminantAnalysis實現的,包含一個引數n_components,表示我們想要返回的特徵數。 為了找出用於n_components的引數值(例如,要保留多少引數),我們可以利用一個事實,explain_variance_ratio_告訴我們每個輸出特徵的解釋方差並且是有序陣列。
具體來說,我們可以執行Linear_iscriminantAnalysis,將n_components設定為None來返回由每個特徵成分的解釋方差比,然後計算需要多少成分才能超過解釋方差的閾值(通常為 0.95 或 0.99)。
# 載入庫
from sklearn import datasets
from sklearn.discriminant_analysis import LinearDiscriminantAnalysis
# 載入鳶尾花資料集
iris = datasets.load_iris()
X = iris.data
y = iris.target
# 建立並執行 LDA
lda = LinearDiscriminantAnalysis(n_components=None)
X_lda = lda.fit(X, y)
# 建立解釋方差比的陣列
lda_var_ratios = lda.explained_variance_ratio_
# 建立函式
def select_n_components(var_ratio, goal_var: float) -> int:
# 設定目前為止的初始解釋方差
total_variance = 0.0
# 設定初始特徵數
n_components = 0
# 對於每個特徵的解釋方差
for explained_variance in var_ratio:
# 將解釋方差新增到總體
total_variance += explained_variance
# 成分數加一
n_components += 1
# 如果我們達到了我們的解釋方差目標
if total_variance >= goal_var:
# 結束迴圈
break
# 返回成分數量
return n_components
# 執行函式
select_n_components(lda_var_ratios, 0.95)
# 1
為 TSVD 選擇最佳數量的成分
# 載入庫
from sklearn.preprocessing import StandardScaler
from sklearn.decomposition import TruncatedSVD
from scipy.sparse import csr_matrix
from sklearn import datasets
import numpy as np
# 載入資料
digits = datasets.load_digits()
# Standardize the feature matrix
X = StandardScaler().fit_transform(digits.data)
# 製作係數矩陣
X_sparse = csr_matrix(X)
# 建立並使用特徵數減一執行 TSVD
tsvd = TruncatedSVD(n_components=X_sparse.shape[1]-1)
X_tsvd = tsvd.fit(X)
# 解釋方差的列表
tsvd_var_ratios = tsvd.explained_variance_ratio_
# 建立函式
def select_n_components(var_ratio, goal_var: float) -> int:
# 設定目前為止的初始解釋方差
total_variance = 0.0
# 設定初始特徵數
n_components = 0
# 對於每個特徵的解釋方差
for explained_variance in var_ratio:
# 將解釋方差新增到總體
total_variance += explained_variance
# 成分數加一
n_components += 1
# 如果我們達到了我們的解釋方差目標
if total_variance >= goal_var:
# 結束迴圈
break
# 返回成分數量
return n_components
# 執行函式
select_n_components(tsvd_var_ratios, 0.95)
# 40
將 LDA 用於降維
# 載入庫
from sklearn import datasets
from sklearn.discriminant_analysis import LinearDiscriminantAnalysis
# 載入鳶尾花資料集
iris = datasets.load_iris()
X = iris.data
y = iris.target
# 建立 LDA,它將資料降維到 1 個特徵
lda = LinearDiscriminantAnalysis(n_components=1)
# 執行 LDA 並使用它轉換特徵
X_lda = lda.fit(X, y).transform(X)
# 列印特徵數
print('Original number of features:', X.shape[1])
print('Reduced number of features:', X_lda.shape[1])
'''
Original number of features: 4
Reduced number of features: 1
'''
## 檢視解釋方差比
lda.explained_variance_ratio_
# array([ 0.99147248])