【機器學習】模型訓練前夜—資料集預處理(概念+圖+實戰)
本文程式碼推薦使用Jupyter notebook跑,這樣得到的結果更為直觀。
缺失資料處理:
# 顯示資料的缺失值
import pandas as pd
from io import StringIO
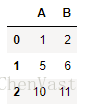
csv_data = '''A,B,C,D
1.0,2.0,3.0,4.0
5.0,6.0,,8.0
10.0,11.0,12.0,''':
# csv_data = unicode(csv_data)
df = pd.read_csv(StringIO(csv_data))
print(df)

# 顯示每列的缺失值數量
df.isnull().sum()

刪除存在缺失值的特徵或者樣本:
# 刪除資料集中包含缺失值的行 df.dropna()

# 刪除資料集中至少包含一個NAN的列,axis=1。
df.dropna(axis=1)
# 只在所有列都為NaN的地方刪除行。
df.dropna(how='all')

# 刪除沒有至少4個非nan值的行。
df.dropna(thresh=4)

# 只有當NaN出現在特定列(這裡:“C”)時,才會刪除行。
df.dropna(subset=['C'])
插值技術:處理資料缺失
最常用的插值技術:均值插補,使用相應的特徵均值來替換缺失值。
from sklearn.preprocessing import Imputer imr = Imputer(missing_values='NaN', strategy='mean', axis=0) imr = imr.fit(df) imputed_data = imr.transform(df.values) print(df.values)
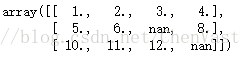
print(imputed_data)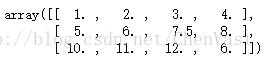
Imputer類的fit方法:對資料集中的引數進行識別並構建相應的資料補齊模型
Imputer類的transform方法:使用剛構建的資料補齊模型對資料集中相應引數的缺失值進行補齊。
資料補齊需要保持維度相同。
處理類別資料:
類別資料分為:標稱特徵、有序特徵
標稱特徵:不具備排序的特性
有序特徵:特徵為有序的或可排序的
例子:
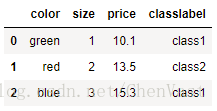
import pandas as pd df = pd.DataFrame([ ['green', 'M', 10.1, 'class1'], ['red', 'L', 13.5, 'class2'], ['blue', 'XL', 15.3, 'class1']]) df.columns = ['color', 'size', 'price', 'classlabel'] print(df)

有序特徵的對映:
類別字串轉整數:
size_mapping = {
'XL': 3,
'L': 2,
'M': 1}
df['size'] = df['size'].map(size_mapping)
print(df)
類標編碼:
類標不是有序的
特定的字串類標,賦予的具體整數值不重要,一般以列舉的方式從0開始設定類標。
import numpy as np
class_mapping = {label:idx for idx,label in enumerate(np.unique(df['classlabel']))}
class_mapping

# 使用對映字典將類標轉為整數
df['classlabel'] = df['classlabel'].map(class_mapping)
print(df)

# 將字典鍵值對倒置,還原為原始資料
inv_class_mapping = {v: k for k, v in class_mapping.items()}
df['classlabel'] = df['classlabel'].map(inv_class_mapping)
print(df)
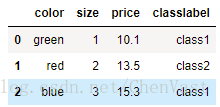
# 使用SKlearn的LabelEncoder類可以快捷的操作整數編碼
from sklearn.preprocessing import LabelEncoder
class_le = LabelEncoder()
y = class_le.fit_transform(df['classlabel'].values)
print (y)
class_le.inverse_transform(y)
標稱特徵上的獨熱編碼
獨熱編碼技術:建立一個新的虛擬特徵,虛擬特徵的每一列各代表標稱標稱資料的一個值。
# 使用OneHotEncoder類實現
from sklearn.preprocessing import OneHotEncoder
ohe = OneHotEncoder(categorical_features=[0])
ohe.fit_transform(X).toarray()

# 使用pandas的get_dummies實現
pd.get_dummies(df[['price', 'color', 'size']])

將資料集劃分為訓練集和測試資料集:
使用pandas,線上從UCI機器學習樣本資料庫讀取開源葡萄酒資料集。
df_wine = pd.read_csv('https://archive.ics.uci.edu/ml/machine-learning-databases/wine/wine.data', header=None)
df_wine.columns = ['Class label', 'Alcohol', 'Malic acid', 'Ash',
'Alcalinity of ash', 'Magnesium', 'Total phenols',
'Flavanoids', 'Nonflavanoid phenols', 'Proanthocyanins',
'Color intensity', 'Hue', 'OD280/OD315 of diluted wines', 'Proline']
print('Class labels', np.unique(df_wine['Class label']))
df_wine.head()

# 使用SKlearn下的model_selection模組中的train_test_split函式
from sklearmodel_selection import train_test_split
X, y = df_wine.iloc[:, 1:].values, df_wine.iloc[:, 0].values
X_train, X_test, y_train, y_test = \
train_test_split(X, y, test_size=0.3, random_state=0)
將陣列中1-13個特徵賦值給X,第一列的類標賦值給變數y。
隨機將X和y各自劃分為訓練集合測試集,
test_size=0.3表示將30%的樣本劃分到X_test 和y_test,剩餘的劃分給X_train和y_train。
劃分訓練集和測試集要儘量保留有價值的資訊。
一般的資料量的資料集劃分法為:60/40,70/30,80/20
大資料量的資料集劃分為:90/10,99/1
將特徵值縮放到相同的區間:
特徵縮放:資料預處理過程中至關重要的一步,為其保證模型的效能最佳。
將不同的特徵縮放到相同的區間:歸一化、標準化
歸一化:將特徵值縮放到[0,1]區間,最小到最大縮放的特例。

x為特定樣本,x min和x max分別為某特徵列的最小值和最大值
案例:
from sklearn.preprocessing import MinMaxScaler
mms = MinMaxScaler()
X_train_norm = mms.fit_transform(X_train)
X_test_norm = mms.transform(X_test)
標準化:將特徵列的均值設為0,方差為1,使得特徵列的值呈標準正態分佈,易於權重更新。保持了異常值所蘊含的有用資訊,使得演算法受到這些值影響最小。
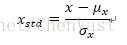
σ和μ分別為某個特徵列的均值和標準差。
案例:
from sklearn.preprocessing import StandardScaler
stdsc = StandardScaler()
X_train_std = stdsc.fit_transform(X_train)
X_test_std = stdsc.transform(X_test)
選擇有意義的特徵值
過擬合(高方差):
模型在訓練集是的表現比測試集上好很多,過擬合於訓練資料。
模型引數對於訓練集的特定觀測值擬合得非常接近
產生的原因:建立給定訓練集上的模型過於複雜
常用降低泛化誤差的方案:
1、 收集更多的訓練資料
2、 正則化引入罰項
3、 選擇相對較少的簡單模型
4、 降低資料的維度
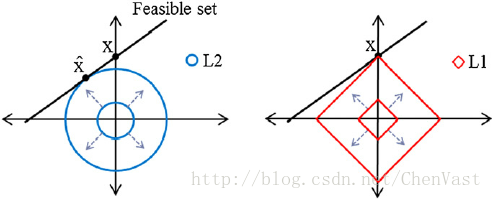
使用L1正則化滿足資料稀疏化:
L1降低模型複雜度
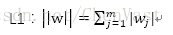
將權重的平方和用絕對值和來代替
L1正則化可以生成稀疏的特徵向量,且大多數權值為0。
通過正則化引數來增加正則化的強度,使得權值向0收縮,降低模型對訓練集的依賴程度
L2的罰項是二次的

SKlearn實現L1正則化程式碼:
from sklearn.linear_model import LogisticRegression
lr = LogisticRegression(penalty='l1', C=0.1)
lr.fit(X_train_std, y_train)
print('Training accuracy:', lr.score(X_train_std, y_train))
print('Test accuracy:', lr.score(X_test_std, y_test))
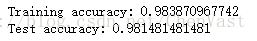
# 訓練和測試的精確度表示未出現過擬合
# 獲得截距項
lr.intercept_
lr.coef_


# 繪製正則化效果圖
import matplotlib.pyplot as plt
%matplotlib inline
fig = plt.figure()
ax = plt.subplot(111)
colors = ['blue', 'green', 'red', 'cyan',
'magenta', 'yellow', 'black',
'pink', 'lightgreen', 'lightblue',
'gray', 'indigo', 'orange']
weights, params = [], []
for c in np.arange(-4, 6):
lr = LogisticRegression(penalty='l1', C=10**c, random_state=0)
lr.fit(X_train_std, y_train)
weights.append(lr.coef_[1])
params.append(10**c)
weights = np.array(weights)
for column, color in zip(range(weights.shape[1]), colors):
plt.plot(params, weights[:, column],
label=df_wine.columns[column+1],
color=color)
plt.axhline(0, color='black', linestyle='--', linewidth=3)
plt.xlim([10**(-5), 10**5])
plt.ylabel('weight coefficient')
plt.xlabel('C')
plt.xscale('log')
plt.legend(loc='upper left')
ax.legend(loc='upper center',
bbox_to_anchor=(1.38, 1.03),
ncol=1, fancybox=True)
# plt.savefig('./figures/l1_path.png', dpi=300)
plt.show()
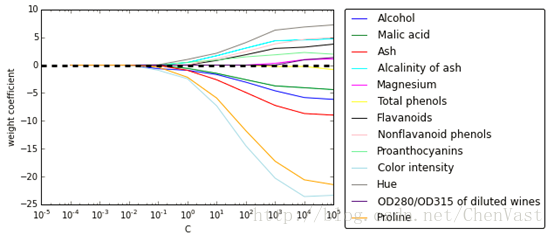
C是正則化引數的倒數。
序列特徵選擇演算法
降低模型複雜度從而解決過擬合的方法是通過特徵選擇進行降維
對未經正則化處理的模型特別有效
降維技術主要分為:特徵降維,特徵提取
序列特徵選擇演算法是一種貪婪演算法,將原始的d維特徵空間壓縮到一個k維的特徵子空間。
經典的序列特徵選擇演算法:序列後向選擇演算法(SBS)
目的:在分類效能衰減最小的約束下,降低原始特徵空間上的資料維度,提高計算效率。
SBS可以在模型面臨過擬合問題時提高模型的預測能力。
SBS演算法理念:SBS依次從特徵集合中刪除某些特徵,直到新的子特徵包含指定數量的特徵
為了確定每一步所需刪除的特徵,需要定義一個最小化的標準衡量函式。
函式準則:比較判定分類器的效能在刪除某個特定特徵前後的差異
由此可知,每一步待刪除的特徵,就是那些能夠使得函式儘可能大的特徵。
演算法步驟:
1、 設k=d進行演算法初始化,d是特徵空間Xd的維度
2、 定義x為滿足標準x=argmax(Xk-x)最大化特徵
3、 將特徵x從特徵集中刪除:X(k-1)=Xk-x,k=k-1
4、 如果k等於目標特徵數量,演算法終止,否則跳到2步。
python實現SBS演算法:
from sklearn.base import clone
from itertools import combinations
import numpy as np
from sklearn.cross_validation import train_test_split
from sklearn.metrics import accuracy_score
class SBS():
def __init__(self, estimator, k_features, scoring=accuracy_score,
test_size=0.25, random_state=1):
self.scoring = scoring
self.estimator = clone(estimator)
self.k_features = k_features
self.test_size = test_size
self.random_state = random_state
def fit(self, X, y):
X_train, X_test, y_train, y_test = \
train_test_split(X, y, test_size=self.test_size,
random_state=self.random_state)
dim = X_train.shape[1]
self.indices_ = tuple(range(dim))
self.subsets_ = [self.indices_]
score = self._calc_score(X_train, y_train,
X_test, y_test, self.indices_)
self.scores_ = [score]
while dim > self.k_features:
scores = []
subsets = []
for p in combinations(self.indices_, r=dim-1):
score = self._calc_score(X_train, y_train,
X_test, y_test, p)
scores.append(score)
subsets.append(p)
best = np.argmax(scores)
self.indices_ = subsets[best]
self.subsets_.append(self.indices_)
dim -= 1
self.scores_.append(scores[best])
self.k_score_ = self.scores_[-1]
return self
def transform(self, X):
return X[:, self.indices_]
def _calc_score(self, X_train, y_train, X_test, y_test, indices):
self.estimator.fit(X_train[:, indices], y_train)
y_pred = self.estimator.predict(X_test[:, indices])
score = self.scoring(y_test, y_pred)
return score
實現SBS應用於SKlearn中KNN分類器:
%matplotlib inline
from sklearn.neighbors import KNeighborsClassifier
import matplotlib.pyplot as plt
knn = KNeighborsClassifier(n_neighbors=2)
# selecting features
sbs = SBS(knn, k_features=1)
sbs.fit(X_train_std, y_train)
# plotting performance of feature subsets
k_feat = [len(k) for k in sbs.subsets_]
plt.plot(k_feat, sbs.scores_, marker='o')
plt.ylim([0.7, 1.1])
plt.ylabel('Accuracy')
plt.xlabel('Number of features')
plt.grid()
plt.tight_layout()
# plt.savefig('./sbs.png', dpi=300)
plt.show()
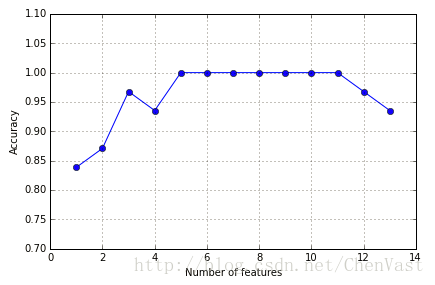
檢視演算法正確率達到100%的特徵:
k5 = list(sbs.subsets_[8])
print(df_wine.columns[1:][k5])
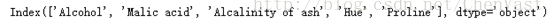
驗證KNN分類器在原始測試集上的表現:
knn.fit(X_train_std, y_train)
print('Training accuracy:', knn.score(X_train_std, y_train))
print('Test accuracy:', knn.score(X_test_std, y_test))
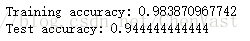
在選定的5個特徵集看KNN效能:
knn.fit(X_train_std[:, k5], y_train)
print('Training accuracy:', knn.score(X_train_std[:, k5], y_train))
print('Test accuracy:', knn.score(X_test_std[:, k5], y_test))

當特徵數量不及葡萄酒資料集原始資料特徵數量一半時,測試集上的預測準確率提高。
SKlearn裡有許多特徵選擇演算法:基於特徵權重的遞迴後向消除演算法、基於特徵重要性的特徵選擇樹方法、單變數統計方法。
通過隨機森林判定特徵的重要性:
from sklearn.ensemble import RandomForestClassifier
feat_labels = df_wine.columns[1:]
forest = RandomForestClassifier(n_estimators=10000,
random_state=0,
n_jobs=-1)
forest.fit(X_train, y_train)
importances = forest.feature_importances_
indices = np.argsort(importances)[::-1]
for f in range(X_train.shape[1]):
print("%2d) %-*s %f" % (f + 1, 30,
feat_labels[f],
importances[indices[f]]))
plt.title('Feature Importances')
plt.bar(range(X_train.shape[1]),
importances[indices],
color='lightblue',
align='center')
plt.xticks(range(X_train.shape[1]),
feat_labels, rotation=90)
plt.xlim([-1, X_train.shape[1]])
plt.tight_layout()
# plt.savefig('./figures/random_forest.png', dpi=300)
plt.show()


